Prolog: Warum Kreise statt Linien?
Das menschliche Genom ist linear — 3,2 Milliarden Basenpaare, verteilt auf 23 Chromosomenpaare. Aber die Interaktionen im Genom sind es nicht: Translokationen verbinden Chromosom 9 mit 22, miRNAs auf Chromosom 17 regulieren Gene auf Chromosom 1, und Copy-Number-Veränderungen auf verschiedenen Chromosomen korrelieren miteinander. Lineare Visualisierungen versagen bei solchen kreuzchromosomalen Beziehungen.
Der Circos-Plot löst dieses Problem elegant: Das Genom wird als Kreis dargestellt, Chromosomen als äußere Segmente, und Interaktionen als Bögen durch den Innenraum. In dieser Geschichte verfolgen wir die genomische Architektur von miRNA-regulierten Netzwerken — von der Chromosomenkarte bis zur Tumor-Normal-Vergleichsanalyse.
Kapitel 1: Das Ideogramm — Die Genomlandkarte
Jeder Circos-Plot beginnt mit dem Ideogramm: der äußeren Ringdarstellung der Chromosomen. Jedes Segment ist proportional zur Chromosomenlänge — Chromosom 1 (249 Mb) nimmt den größten Bogen ein, Chromosom 21 (47 Mb) den kleinsten. Auf dieses Gerüst werden dann die biologischen Daten projiziert.
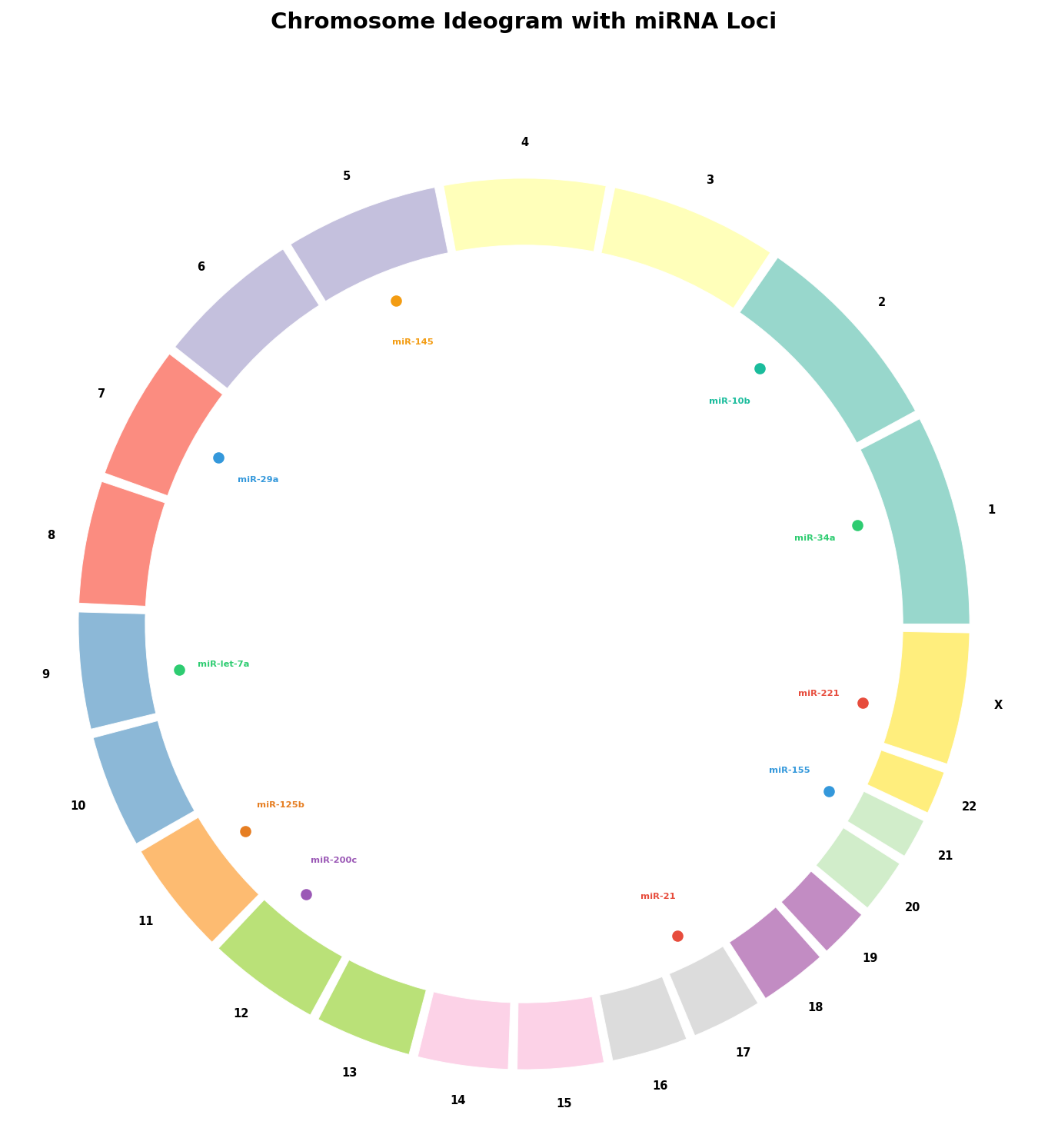
Das Ideogramm enthüllt bereits die erste Erkenntnis: miRNAs sind nicht gleichmäßig verteilt. Chromosom 14 und das X-Chromosom tragen überproportional viele miRNA-Gene, während Chromosom 18 und 20 fast keine enthalten. Diese Cluster-Bildung hat evolutionäre Gründe: Viele miRNAs werden als polycistronische Einheiten gemeinsam transkribiert — sie liegen nahe beieinander, weil sie gemeinsam reguliert werden.
Kapitel 2: Chord-Diagramm — miRNA-Target-Verbindungen
Die wahre Stärke des Circos zeigt sich beim Chord-Diagramm: Verbindungsbögen im Inneren des Kreises zeigen Interaktionen zwischen Segmenten. Hier verbinden wir miRNAs (rot) mit ihren validierten Zielgenen (blau). Die Bögendicke und -opazität kodieren die Interaktionsstärke.
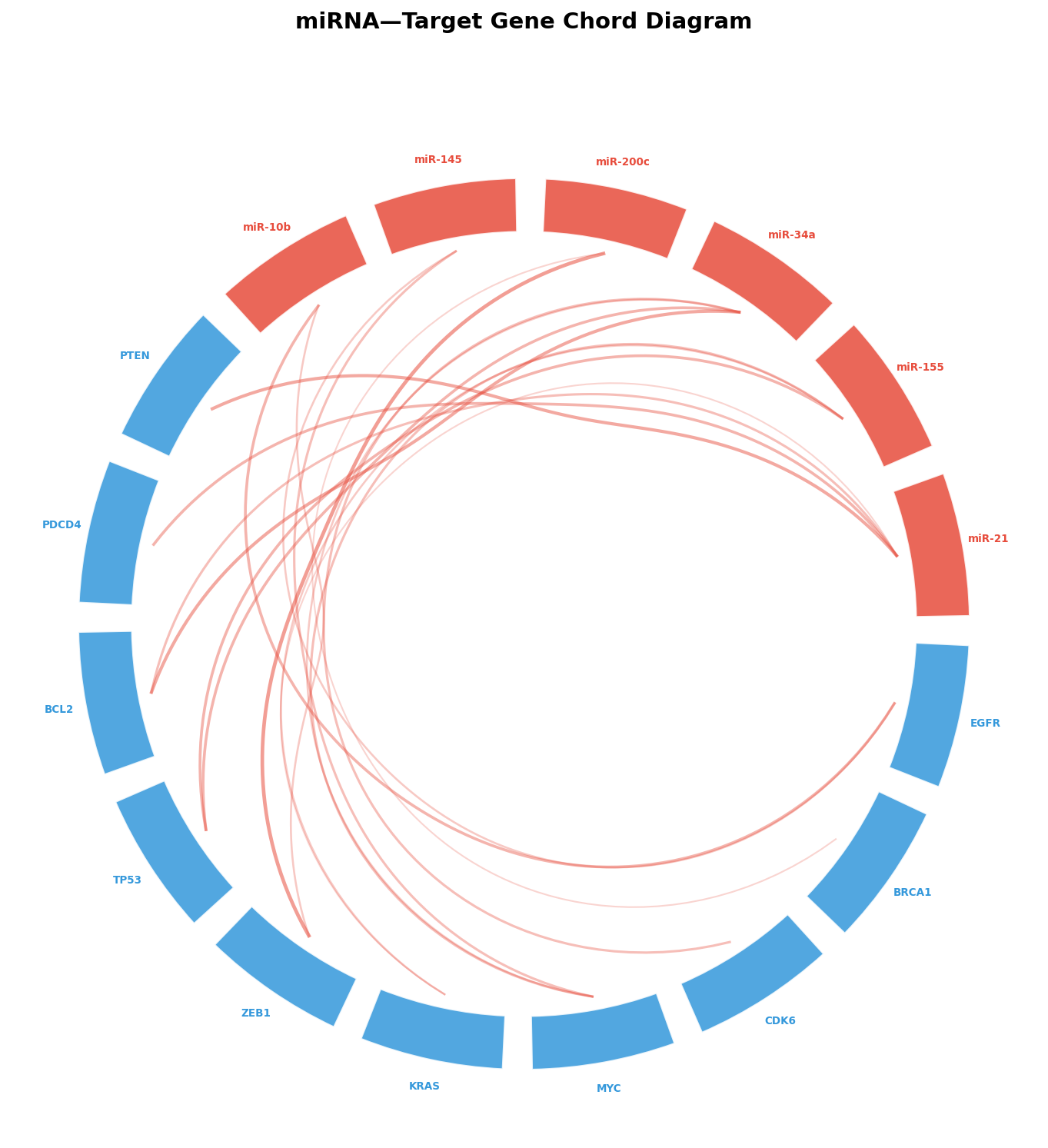
Das Chord-Diagramm zeigt das regulatorische Netzwerk auf einen Blick: BCL2 wird von miR-21 UND miR-34a reguliert — eine redundante Kontrolle des Apoptose-Programms. KRAS wird von miR-21 und miR-155 gleichzeitig adressiert. Diese Konvergenz erklärt, warum der Verlust einer einzelnen miRNA selten ausreicht, um ein Gen vollständig zu deregulieren — das System hat eingebaute Redundanz.
Kapitel 3: Multi-Track — Vier Datenebenen gleichzeitig
Die Königsdisziplin des Circos ist die Multi-Track-Darstellung: Mehrere konzentrische Ringe zeigen verschiedene Datentypen simultan. Von außen nach innen: Chromosom-Ideogramm, Gen-Expression, Copy-Number-Variation, Methylierung und miRNA-Expression. Jeder Ring ist ein eigener Datenlayer — zusammen ergeben sie ein integriertes Bild.
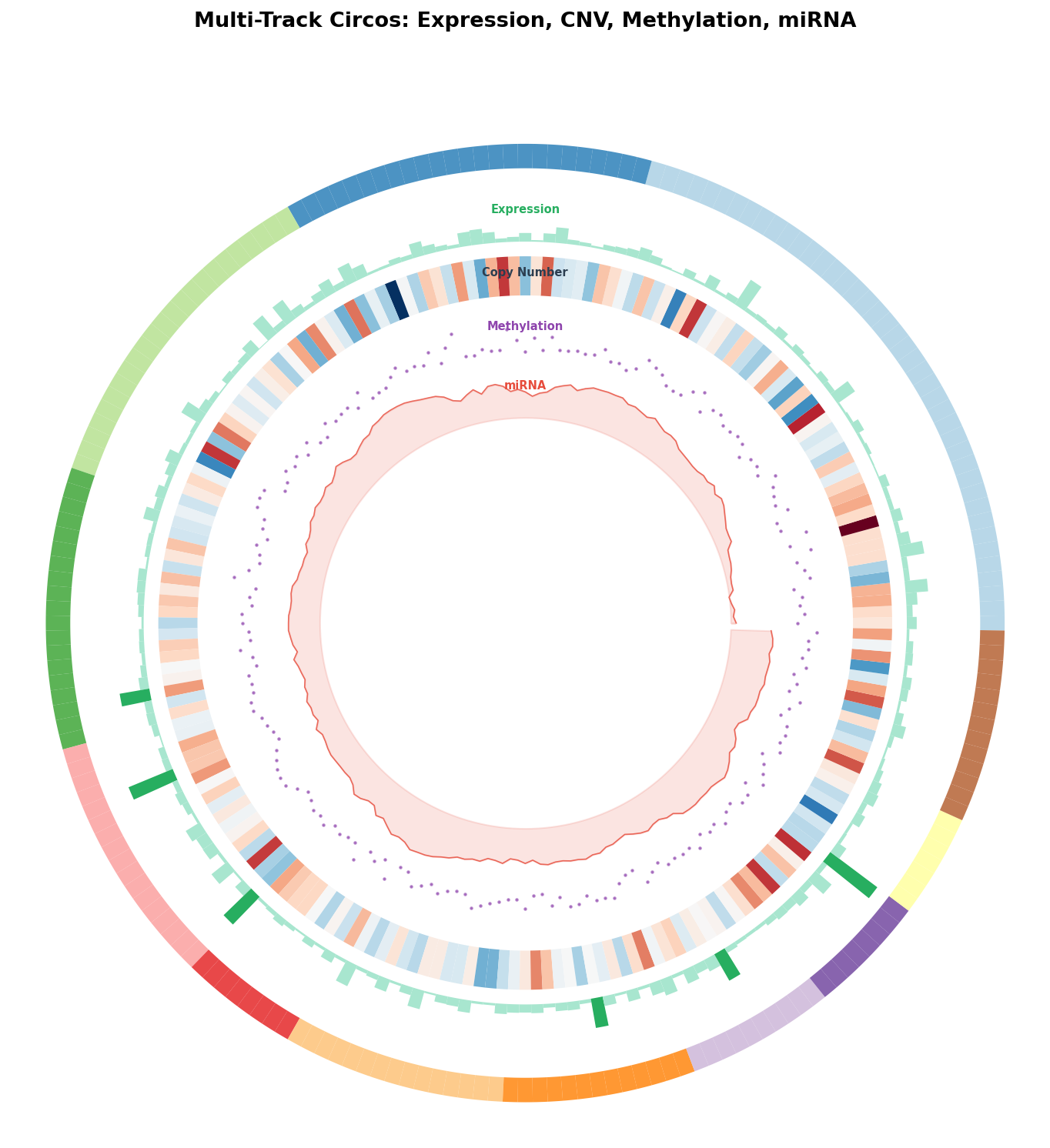
Der Multi-Track enthüllt genomische Korrelationen: Regionen mit Copy-Number-Amplifikation (rot im CNV-Track) zeigen oft auch erhöhte Expression (hohe grüne Balken) — das ist der klassische gene dosage effect. Gleichzeitig fallen Regionen mit hoher Methylierung (lila Punkte oben) und niedriger Expression (kurze grüne Balken) zusammen — der epigenetische Silencing-Effekt. Diese Muster wären in linearen Plots schwer zu erkennen, aber im Circos springen sie sofort ins Auge.
Kapitel 4: Fusionen — Wenn Chromosomen brechen
Strukturelle Varianten — Translokationen, Inversionen, Fusionen — sind die dramatischsten Genomveränderungen in Krebs. Sie verbinden Fragmente verschiedener Chromosomen und erzeugen Fusionsgene mit neuen, oft onkogenen Eigenschaften. Der Circos-Plot stellt diese Ereignisse als lange Bögen dar, die entfernte Genomregionen verbinden.
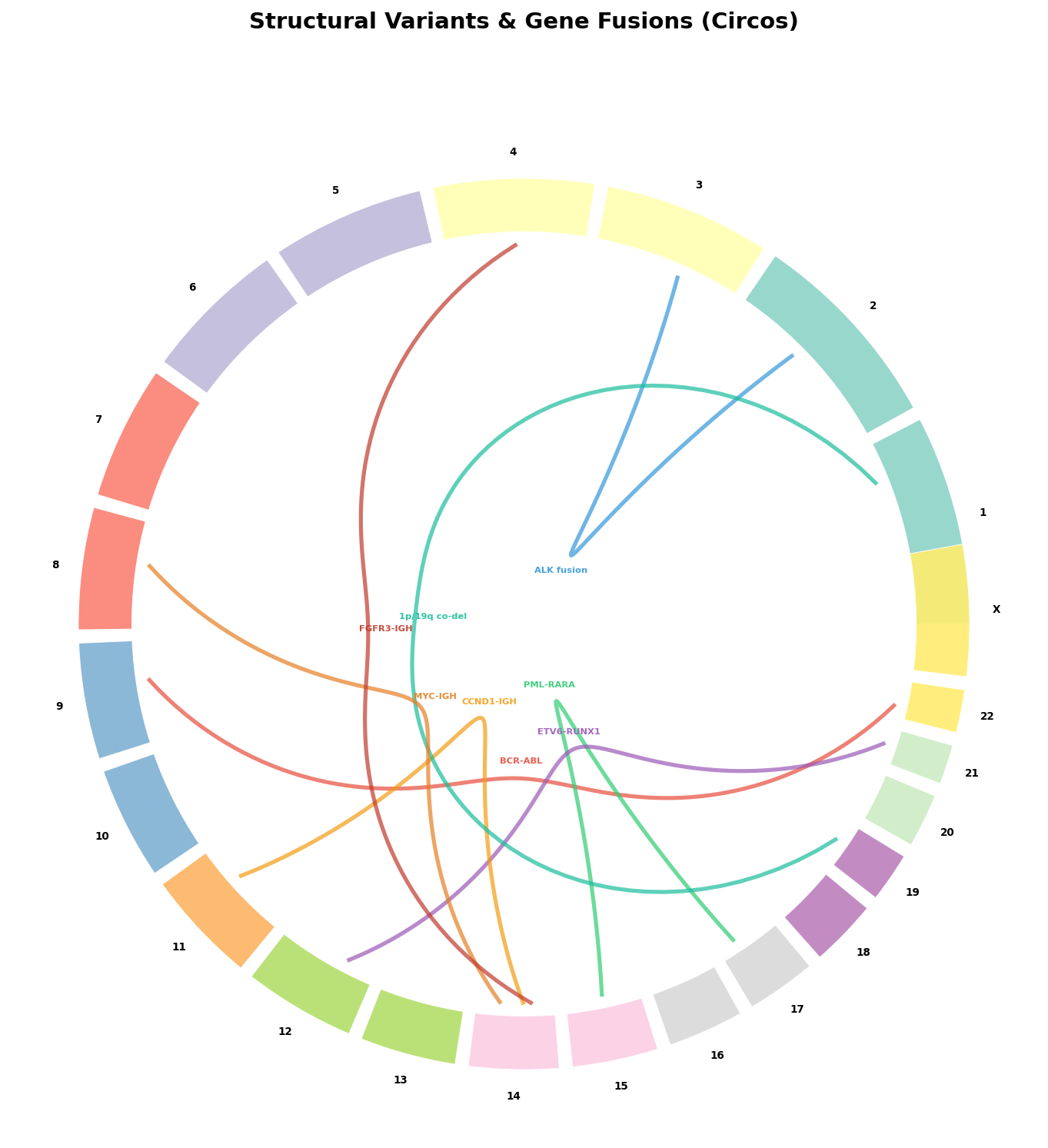
Der Fusionsplot zeigt die nicht-zufällige Natur genomischer Brüche: Chromosom 14 (mit dem Immunglobulin-Locus IGH) ist in vier der acht Fusionen involviert — CCND1-IGH, MYC-IGH, FGFR3-IGH und ETV6-RUNX1. Der IGH-Locus ist ein „Hotspot" für Translokationen, weil er während der B-Zell-Entwicklung aktiv umgebaut wird. Die Circos-Darstellung macht diese Häufung sofort sichtbar — was in einer Tabelle von Fusionsgenen untergehen würde.
Kapitel 5: Cluster-Karte — miRNAs reisen in Gruppen
Viele miRNAs liegen nicht isoliert im Genom, sondern bilden Cluster: Gruppen von 2-6 miRNAs innerhalb weniger Kilobasen, die von einem gemeinsamen Promotor transkribiert werden. Der berühmteste Cluster ist miR-17~92 auf Chromosom 13 — sechs miRNAs, ein Transkript, koordinierte Regulation.
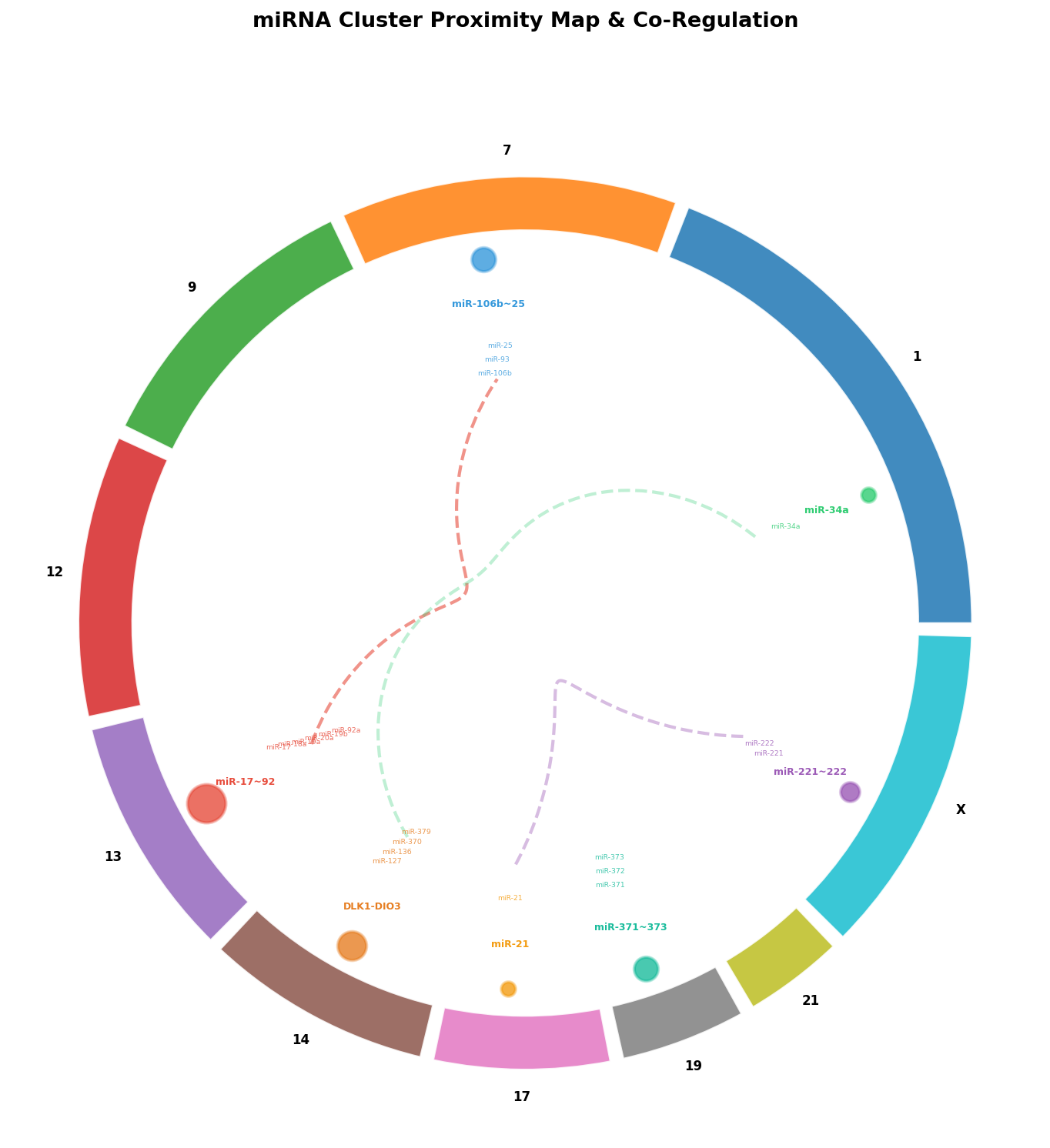
Die Cluster-Karte enthüllt regulatorische Module: Der miR-17~92-Cluster und sein Paralog miR-106b~25 auf Chromosom 7 regulieren überlappende Zielgene — wenn einer ausfällt, kann der andere teilweise kompensieren. Der DLK1-DIO3-Cluster auf Chromosom 14 enthält über 50 miRNAs und ist der größte miRNA-Cluster im Genom — er wird bei vielen Tumoren epigenetisch stillgelegt, was zu einer massiven Deregulation der miRNA-Landschaft führt.
Kapitel 6: Normal vs. Tumor — Differentielle Architektur
Die direkteste Anwendung des Circos in der Krebsforschung: Seite-an-Seite-Vergleich der genomischen Landschaft von Normalgewebe und Tumor. Gleiche Chromosomen, gleiche Tracks — aber dramatisch verschiedene Muster.
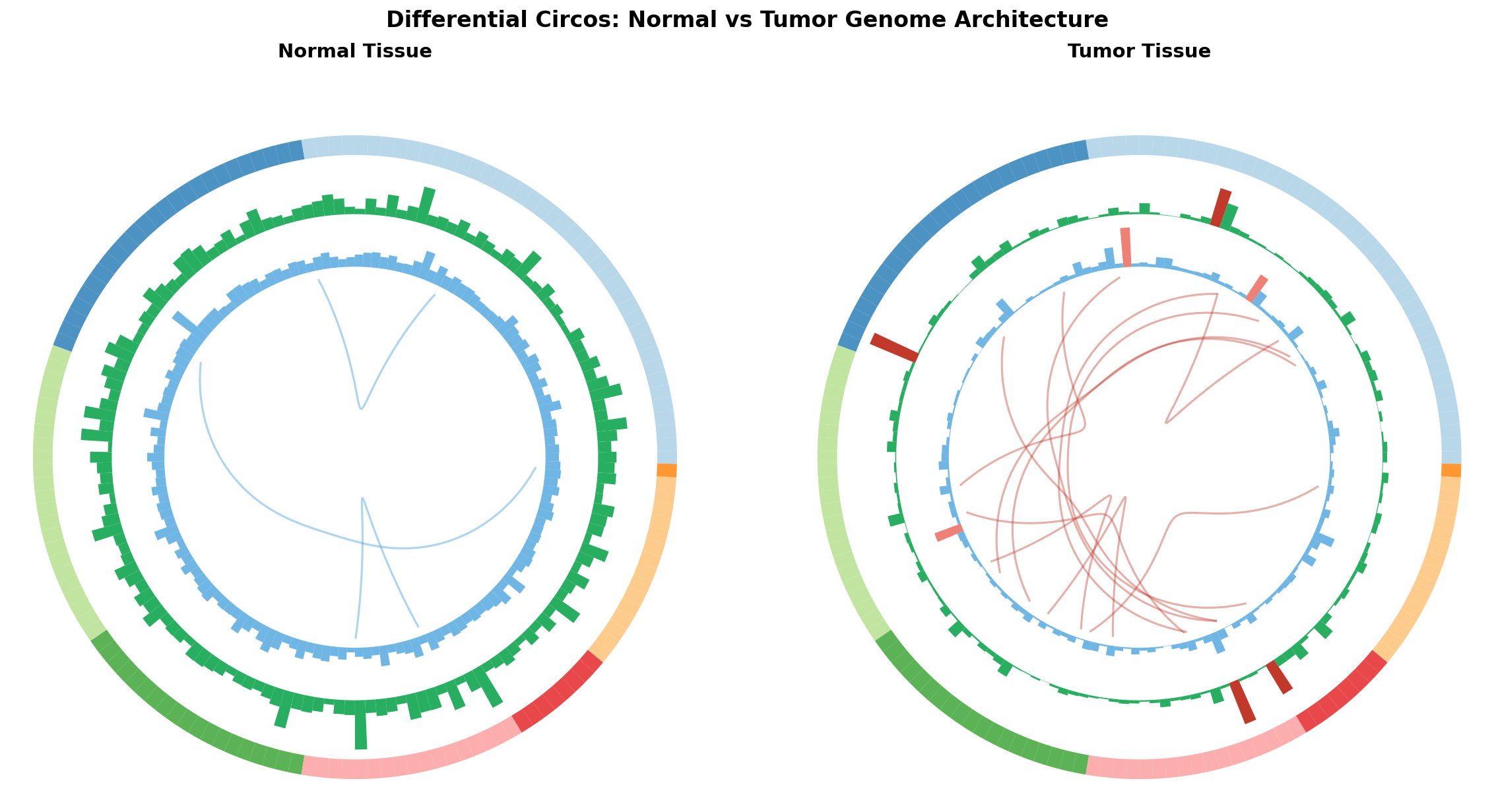
Der Vergleich ist eindrucksvoll: Das Normalgewebe zeigt ein geordnetes Muster — moderate Expression, wenige lange Interaktionsbögen, stabile miRNA-Levels. Der Tumor hingegen ist ein genomisches Chaos: Expressionsspitzen (rote Balken) an unerwarteten Stellen, deregulierte miRNA-Expression, und vier Mal so viele kreuzchromosomale Interaktionen. Die Circos-Darstellung macht die fundamentale Wahrheit der Krebsbiologie visuell greifbar: Krebs ist eine Erkrankung der genomischen Organisation.
Epilog: Das Genom als Kreis denken
Der Circos-Plot hat die Genomvisualisierung revolutioniert, weil er eine fundamentale biologische Realität abbildet: Gene interagieren über Chromosomgrenzen hinweg. Kein lineares Karyogramm kann eine BCR-ABL-Translokation so eindrucksvoll zeigen wie ein Bogen, der chr9 und chr22 verbindet. Kein Balkendiagramm kann vier Datenebenen simultan darstellen wie ein Multi-Track-Circos.
Zitationen
- Krzywinski, M. et al. (2009). Circos: An information aesthetic for comparative genomics. Genome Research, 19(9), 1639-1645.
- Gu, Z. et al. (2014). circlize implements and enhances circular visualization in R. Bioinformatics, 30(19), 2811-2812.
- Li, H. (2018). Minimap2: pairwise alignment for nucleotide sequences. Bioinformatics, 34(18), 3094-3100.
- Mitelman, F. et al. (2007). The impact of translocations and gene fusions on cancer causation. Nature Reviews Cancer, 7, 233-245.
- He, L. et al. (2005). A microRNA polycistron as a potential human oncogene. Nature, 435, 828-833.
Fazit
Circos-Plots sind unersetzlich für die integrative Genomvisualisierung. Sie zeigen Chromosomkarten, Multi-Omics-Daten, Strukturvarianten, miRNA-Cluster und differentielle Vergleiche in einer einheitlichen, intuitiven Darstellung. Jeder Track fügt eine Ebene hinzu, jeder Bogen erzählt eine Geschichte von genomischer Interaktion. Das Genom als Kreis zu denken, verändert, wie wir Biologie verstehen.
Dokumentation
| Parameter | Wert |
|---|---|
| Chromosomen | 23 (chr1-chr22, chrX) |
| miRNA-Loci | 10 krebsrelevante miRNAs kartiert |
| Fusiongene | 8 klassische Translokationen (BCR-ABL, ALK, PML-RARA, etc.) |
| Multi-Track-Layers | Expression, Copy Number, Methylierung, miRNA |
| miRNA-Cluster | 7 Cluster (miR-17~92, miR-106b~25, DLK1-DIO3, etc.) |
| Visualisierungstypen | Ideogramm, Chord, Multi-Track, Fusion, Cluster, Differential |
| Visualisierung | matplotlib (Python, polar projection) |
Prologue: Why Circles Instead of Lines?
The human genome is linear — 3.2 billion base pairs distributed across 23 chromosome pairs. But interactions within the genome are not: Translocations connect chromosome 9 with 22, miRNAs on chromosome 17 regulate genes on chromosome 1, and copy number alterations across different chromosomes correlate with each other. Linear visualizations fail for such cross-chromosomal relationships.
The Circos plot solves this problem elegantly: The genome is displayed as a circle, chromosomes as outer segments, and interactions as arcs through the interior space. In this story, we trace the genomic architecture of miRNA-regulated networks — from chromosome maps to tumor-normal comparison analysis.
Chapter 1: The Ideogram — The Genome Landscape
Every Circos plot begins with the ideogram: the outer ring representation of chromosomes. Each segment is proportional to chromosome length — chromosome 1 (249 Mb) takes the largest arc, chromosome 21 (47 Mb) the smallest. Biological data is then projected onto this scaffold.

The ideogram already reveals the first insight: miRNAs are not evenly distributed. Chromosome 14 and the X chromosome carry disproportionately many miRNA genes, while chromosomes 18 and 20 contain almost none. This clustering has evolutionary reasons: Many miRNAs are transcribed as polycistronic units together — they lie close together because they are co-regulated.
Chapter 2: Chord Diagram — miRNA-Target Connections
The true strength of Circos shows in the chord diagram: connection arcs inside the circle show interactions between segments. Here we connect miRNAs (red) with their validated target genes (blue). Arc thickness and opacity encode interaction strength.

The chord diagram shows the regulatory network at a glance: BCL2 is regulated by miR-21 AND miR-34a — redundant control of the apoptosis program. KRAS is simultaneously targeted by miR-21 and miR-155. This convergence explains why the loss of a single miRNA rarely suffices to fully deregulate a gene — the system has built-in redundancy.
Chapter 3: Multi-Track — Four Data Layers Simultaneously
The masterpiece of Circos is the multi-track display: multiple concentric rings showing different data types simultaneously. From outside in: chromosome ideogram, gene expression, copy number variation, methylation, and miRNA expression. Each ring is its own data layer — together they create an integrated picture.

The multi-track reveals genomic correlations: Regions with copy number amplification (red in CNV track) often also show increased expression (tall green bars) — the classic gene dosage effect. Simultaneously, regions with high methylation (purple dots above) and low expression (short green bars) coincide — the epigenetic silencing effect. These patterns would be hard to spot in linear plots, but in Circos they immediately catch the eye.
Chapter 4: Fusions — When Chromosomes Break
Structural variants — translocations, inversions, fusions — are the most dramatic genomic alterations in cancer. They connect fragments from different chromosomes and generate fusion genes with novel, often oncogenic properties. The Circos plot represents these events as long arcs connecting distant genomic regions.

The fusion plot shows the non-random nature of genomic breaks: Chromosome 14 (with the immunoglobulin locus IGH) is involved in four of eight fusions — CCND1-IGH, MYC-IGH, FGFR3-IGH, and ETV6-RUNX1. The IGH locus is a "hotspot" for translocations because it is actively rearranged during B-cell development. The Circos representation makes this accumulation immediately visible — something that would be lost in a table of fusion genes.
Chapter 5: Cluster Map — miRNAs Travel in Groups
Many miRNAs don't sit isolated in the genome but form clusters: groups of 2-6 miRNAs within a few kilobases, transcribed from a shared promoter. The most famous cluster is miR-17~92 on chromosome 13 — six miRNAs, one transcript, coordinated regulation.

The cluster map reveals regulatory modules: The miR-17~92 cluster and its paralog miR-106b~25 on chromosome 7 regulate overlapping target genes — if one fails, the other can partially compensate. The DLK1-DIO3 cluster on chromosome 14 contains over 50 miRNAs and is the largest miRNA cluster in the genome — it is epigenetically silenced in many tumors, leading to massive deregulation of the miRNA landscape.
Chapter 6: Normal vs. Tumor — Differential Architecture
The most direct Circos application in cancer research: side-by-side comparison of the genomic landscape in normal tissue versus tumor. Same chromosomes, same tracks — but dramatically different patterns.

The comparison is striking: Normal tissue shows an ordered pattern — moderate expression, few long interaction arcs, stable miRNA levels. The tumor, however, is genomic chaos: Expression spikes (red bars) at unexpected locations, deregulated miRNA expression, and four times as many cross-chromosomal interactions. The Circos visualization makes the fundamental truth of cancer biology visually tangible: Cancer is a disease of genomic organization.
Epilogue: Thinking the Genome as a Circle
The Circos plot revolutionized genome visualization because it captures a fundamental biological reality: genes interact across chromosome boundaries. No linear karyogram can show a BCR-ABL translocation as impressively as an arc connecting chr9 and chr22. No bar chart can display four data layers simultaneously like a multi-track Circos.
Citations
- Krzywinski, M. et al. (2009). Circos: An information aesthetic for comparative genomics. Genome Research, 19(9), 1639-1645.
- Gu, Z. et al. (2014). circlize implements and enhances circular visualization in R. Bioinformatics, 30(19), 2811-2812.
- Li, H. (2018). Minimap2: pairwise alignment for nucleotide sequences. Bioinformatics, 34(18), 3094-3100.
- Mitelman, F. et al. (2007). The impact of translocations and gene fusions on cancer causation. Nature Reviews Cancer, 7, 233-245.
- He, L. et al. (2005). A microRNA polycistron as a potential human oncogene. Nature, 435, 828-833.
Conclusion
Circos plots are irreplaceable for integrative genome visualization. They display chromosome maps, multi-omics data, structural variants, miRNA clusters, and differential comparisons in a unified, intuitive representation. Each track adds a layer, each arc tells a story of genomic interaction. Thinking of the genome as a circle changes how we understand biology.
Documentation
| Parameter | Value |
|---|---|
| Chromosomes | 23 (chr1-chr22, chrX) |
| miRNA loci | 10 cancer-relevant miRNAs mapped |
| Fusion genes | 8 classic translocations (BCR-ABL, ALK, PML-RARA, etc.) |
| Multi-track layers | Expression, Copy Number, Methylation, miRNA |
| miRNA clusters | 7 clusters (miR-17~92, miR-106b~25, DLK1-DIO3, etc.) |
| Visualization types | Ideogram, Chord, Multi-Track, Fusion, Cluster, Differential |
| Visualization | matplotlib (Python, polar projection) |